Python 官方文档:入门教程 => 点击学习
目录K-Means聚类算法介绍K-Means聚类算法基础原理K-Means聚类算法实现流程开始做一个简单的聚类数据导入数据探索 开始聚类查看输出结果聚类质心K-Means聚
K-Means又称为K均值聚类算法,属于聚类算法中的一种,而聚类算法在机器学习算法中属于无监督学习,在业务中常常会结合实际需求与业务逻辑理解来完成建模;
无监督学习:训练时只需要特征矩阵X,不需要标签;
K-Means聚类算法是聚类算法家族中的典型代表,同时也是最简单的算法,接下来为大家简单地介绍聚类算法基本原理:
将一组存在N个样本的特征矩阵X划分为K个无交集的簇,每一个簇中含有多个数据,每一个数据代表着一个样本,在同一个簇中的数据即被算法认为是同一类;
- N:假设为样本数量;
- K:假设为聚类簇的数量;
- 簇:类似于集合,也可以通俗地理解成一个小组,不同小组等于不同分类;
而一个簇中的所有数据的均值,被称为这个簇的质心,质心的维度与特征矩阵X的维度相同,如特征矩阵X是三维数据集,质心也就是一个三维的坐标,如此类推至更高维度;
步骤一:随机在N个样本中抽取K个作为初始的质心;
步骤二:开始遍历除开质心外的所有样本点,将其分配至距离它们最近的质心,每一个质心以及被分配至其下的样本点视为一个簇(或者说一个分类),这样便完成了一次聚类;
步骤三:对于每一个簇,重新计算簇内所有样本点的平均值,取结果为新的质心;
步骤四:比对旧的质心与新的质心是否再发生变化,若发生变化,按照新的质心从步骤二开始重复,若没发生变化,聚类完成;
关键要点:不断地为样本点寻找质心,然后更新质心,直至质心不再变化;
环境说明:本文实际案例中使用Jupyter环境下运行(安装与使用可自行百度);
做数据分析前,首先第一步是导入数据,可以利用pandas内的read_csv函数来导入数据;
首先,导入所需要用到的类,并使用read_csv函数导入案例数据:
import numpy as np
import pandas as pd
data = pd.read_csv(r'D:\Machine_learning\KMeans\client_data.csv')
# 使用pandas中的read_csv函数导入数据集后,默认格式为DataFrame
# 直接查看当前数据集长什么样子
data.head()数据打开后会发现大概长这样:
交易额 成交单量 最近交易时间
0 76584.92 294 64
1 94581.00 232 1
2 51037.60 133 1
3 43836.00 98 1
4 88032.00 95 2
# 若表头项为中文时,可能出现乱码情况,请自行百度解决,或直接修改为英文;
先探索数据类型:
# 探索数据类型
data.info()
# 输出结果:
<class 'pandas.core.frame.DataFrame'>
RangeIndex: 8011 entries, 0 to 8010
Data columns (total 3 columns):
# Column Non-Null Count Dtype
--- ------ -------------- -----
0 交易额 8011 non-null float64
1 成交单量 8011 non-null int64
2 最近交易时间 8011 non-null int64
dtypes: float64(1), int64(2)
memory usage: 187.9 KB由于sklearn中K-Means聚类算法仅支持二维数组运算,所以要先将数据集转化为二维数组:
data = np.array(data,type(float))
# 查看数据集
data
——————————————————————————————————————————————————
# 输出结果:
array([[76584.92, 294.0, 64.0],
[94581.0, 232.0, 1.0],
[51037.6, 133.0, 1.0],
...,
[0.0, 0.0, 180.0],
[0.0, 0.0, 180.0],
[0.0, 0.0, 180.0]], dtype=object)查看数组结构:
# 查看数组结构
data.shape
——————————————————————————————————————————————————
# 输出结果:
(8011, 3)数据集导入完成后,现在调用sklearn完成简单的聚类:
from sklearn.cluster import KMeans
X = data
# 实例化K-Means算法模型,先使用5个簇尝试聚类
cluster = KMeans(n_clusters=5, random_state=0)
# 使用数据集X进行训练
cluster = cluster.fit(X)
# 调用属性labels_,查看聚类结果
cluster.labels_
——————————————————————————————————————————————————
# 输出结果:
array([4, 4, 1, ..., 0, 0, 0])查看输出结果的数组结构:
# 查看预测结果的数据结构
cluster.labels_.shape
——————————————————————————————————————————————————
# 输出结果:
(8011,)分类结果的数组结构为(8011,),刚好对应着8011个样本的预测分类结果;
再次确认目标分类结果只有5类,可以使用numpy中的unique()函数实现:
# 查看数组中存在的类别(对一维数组去重)
np.unique(cluster.labels_)
————————————————————————————————————————
# 输出结果:
array([0, 1, 2, 3, 4])输出结果0~4中分别代表着5个不同的分类;
查看预测结果中每一分类的数量:
# 查看每一分类结果的数量
pd.value_counts(cluster.labels_)
——————————————————————————————————————————
0 7068
2 688
4 198
1 38
3 19
dtype: int64分类为0的数据占比较大(约88%),这部分数据数据实际行业应用中的长尾数据,这类用户对平台几乎没有任何价值贡献;
聚类质心代表每一个分类簇的中心,某种意义上讲,质心坐标可以代表着这一个簇的普遍特征,质心可以通过调用属性cluster_centers_来查看:
# 查看质心
cluster.cluster_centers_
——————————————————————————————————————————————————————————
# 输出结果:
array([[3.40713759e+02, 7.43350311e-01, 1.48025750e+02],
[4.30125087e+04, 4.70000000e+01, 2.03947368e+01],
[6.06497324e+03, 9.37354651e+00, 3.55159884e+01],
[7.57037853e+04, 7.84736842e+01, 1.52631579e+01],
[1.80933537e+04, 2.34040404e+01, 1.49444444e+01]])输出结果中分别对应着0~4五种分类的普遍数据特征;
当我们完成聚类建模后,怎么知道聚类的效果好不好,这时我们便需要「评估指标」来评价模型的优劣,并根据此来调整参数;
对于聚类算法的评估指标,从大方向上区分为两种:真实标签已知与真实标签未知;
即我们对于每一个样本的标签Y都是已知的,但是这种情况在实际的业务中几乎是不存在的,若标签已知,使用分类算法(如随机森林、SVM等)在各个方面来说都会更加合适;
在sklearn中的类为sklearn.metrics.adjusted_rand_score(y_true, y_pred)
y_true:代表测试集中一个样本的真实标签;
y_pred:使用测试集中样本调用预测接口的预测结果(上文中使用的cluster.labels_);
调整兰德系数的取值在[-1,1]:数值越接近1越好,大于0时聚类效果较为优秀,小于0时代表簇内差异巨大甚至相互独立,模型几乎不可用;
由于案例数据集中真实标签是未知的,故不在此展示;
即我们对每一个样本的标签Y都是未知的,我们事先不知道每一个样本是属于什么分类,这种情况才是符合我们实际业务中真实使用聚类算法的场景;
在sklearn中的类为:
返回轮廓系数的均值:sklearn.metrics.silhouette_score(X, y_pred);
返回数据集中每个样本自身的轮廓系数:sklearn.metrics.silhouette_sample(X, y_pred);
轮廓系数的取值在(-1,1):
对于某一样本点来说,当值越接近1时就代表自身与所在的簇中其他样本越相似,并且与其他簇中的样本不相似,而当值越接近-1时则代表与上述内容相反;综述,轮廓系数越接近1越好,负数则表示聚类效果非常差;
那接下来看看轮廓系数在刚才的聚类中效果如何:
# 导入轮廓系数所需要的库
from sklearn.metrics import silhouette_score
from sklearn.metrics import silhouette_samples
# 查看轮廓系数均值
silhouette_score(X,cluster.labels_)
——————————————————————————————————————————————————
# 输出结果
0.8398497410297728
——————————————————————————————————————————————————
# 查看每一样本轮廓系数
silhouette_samples(X,cluster.labels_)
——————————————————————————————————————————————————
# 输出结果
array([0.94301872, 0.94301872, 0.94301872, ..., 0.64706719, 0.60820687,
0.58272791])
——————————————————————————————————————————————————
# 查看样本轮廓系数结果的数组结构
silhouette_samples(X,cluster.labels_).shape
——————————————————————————————————————————————————
# 输出结果
(8011,)本次聚类的轮廓系数为0.84,表示聚类效果良好;
样本轮廓系数的数据结构可以看出:数组中每一个输出结果对应着每一个样本的轮廓系数,共8011个;
sklearn中的类:sklearn.metrics.calinski_haabasz_score (X, y_pred);
卡林斯基-哈拉巴斯指数的数值无上限,且对于模型效果来说越高越好,而由于无上限的特性,导致只能用作对比,而无法快速知晓模型效果是否好;
可以看看轮廓系数在刚才的聚类中效果如何:
# 调用所需要的类
from sklearn.metrics import calinski_harabasz_score
calinski_harabasz_score(X,cluster.labels_)
———————————————————————————————————————————————————————
# 输出结果
31777.971149699857输出的结果为31778,那究竟效果如何?因为没有对照组,所以无法得知,如果有兴趣的小伙伴可以在调整参数的时候使用对照组试试效果;
需要绘制轮廓系数分布图,先导入所需用到的库:
import matplotlib.pyplot as plt
import matplotlib.cm as cm绘制轮廓系数分布图
使用for循环分别对2~8个簇的情况画出轮廓系数分布图:
for n_clusters in [2,3,4,5,6,7,8]:
n_clusters = n_clusters
# 设置画布
fig, ax1 = plt.subplots(1)
# 设置画布尺寸
fig.set_size_inches(18, 7)
# 设置画布X轴
ax1.set_xlim([-0.1, 1])
# 设置画布Y轴:X.shape[0]代表着柱状的宽度,(n_clusters + 1) * 10代表着柱与柱之间的间隔
ax1.set_ylim([0, X.shape[0] + (n_clusters + 1) * 10])
# 模型实例化
clusterer = KMeans(n_clusters=n_clusters, random_state=100)
# 开始训练模型
clusterer = clusterer.fit(X)
# 提取训练结果中的预测标签
cluster_labels = clusterer.labels_
# 提取训练结果中的轮廓系数均值
silhouette_avg = silhouette_score(X, cluster_labels)
# 打印出当前的簇数与轮廓系数均值
print("簇数为", n_clusters,
",轮廓系数均值为", silhouette_avg)
# 提取每一个样本的轮廓系数
sample_silhouette_values = silhouette_samples(X, cluster_labels)
# 设置Y轴的起始坐标
y_lower = 10
# 添加一个循环,把每一个样本的轮廓系数画在图中
for i in range(n_clusters):
# 提取第i个簇下的所有样本轮廓系数
ith_cluster_silhouette_values = sample_silhouette_values[cluster_labels == i]
# 对样本的轮廓系数进行排序(降序)
ith_cluster_silhouette_values.sort()
# 设置当前簇的柱状宽度(使用样本数量)以便于设置下一个簇的起始坐标
size_cluster_i = ith_cluster_silhouette_values.shape[0]
# 设置Y轴第i个簇的起始坐标
y_upper = y_lower + size_cluster_i
# 设置颜色
color = cm.nipy_spectral(float(i)/n_clusters)
# 画图
ax1.fill_betweenx(np.arange(y_lower, y_upper)
,ith_cluster_silhouette_values
,facecolor=color
,alpha=0.7
)
ax1.text(-0.05
, y_lower + 0.5 * size_cluster_i
, str(i))
y_lower = y_upper + 10
# 设置图的标题
ax1.set_title("The silhouette plot for the various clusters.")
ax1.set_xlabel("The silhouette coefficient values")
ax1.set_ylabel("Cluster label")
# 添加轮廓系数均值线,使用虚线
ax1.axvline(x=silhouette_avg, color="red", linestyle="--")
ax1.set_yticks([])
ax1.set_xticks([-0.1, 0, 0.2, 0.4, 0.6, 0.8, 1])
plt.show()输出结果:
簇数为 2 ,轮廓系数均值为 0.9348704011138467:
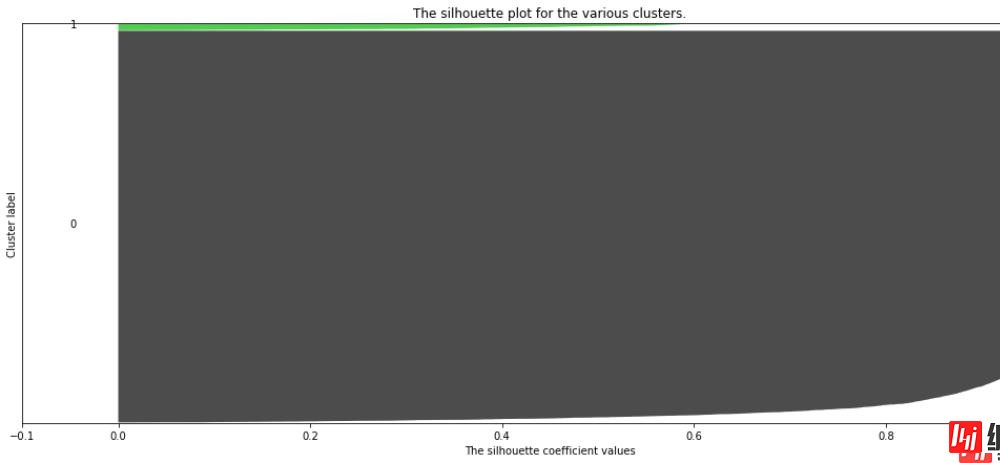
簇数为 3 ,轮廓系数均值为 0.8889120986545176:

簇数为 4 ,轮廓系数均值为 0.8432045328349393:

簇数为 5 ,轮廓系数均值为 0.8397653971050274:

簇数为 6 ,轮廓系数均值为 0.8217141668609508:

簇数为 7 ,轮廓系数均值为 0.7995236853252528:

簇数为 8 ,轮廓系数均值为 0.7995236853252528:

从本次的输出结果中可知,当簇数量为2时,会存在最大的轮廓系数均值,是否簇数量为2就是最佳的参数呢?
答案必须是否定的,我们可以通过轮廓系数分部图看到,基本上每一个图内都会有一片面积很大的块,这就是长尾数据带来的,因为他们基本都集中在一个点上,所以导致整体轮廓系数均值“被平均”得很大,这样的状况也是很多实际业务数据中常常会碰到的;
既然由于长尾数据对轮廓系数带来较大偏差,那咱们的思路可以把长尾数据剔除掉,仅计算非长尾数据(数据分析需要在不同的具体场景下有不同的思路,以下仅是一种思路举例);
当簇数量为3时:
# 实例化,训练模型
n_clusters = 3
clusterer = KMeans(n_clusters=n_clusters, random_state=100)
clusterer = clusterer.fit(X)
# 查看训练结果
pd.value_counts(clusterer.labels_)
————————————————————————————————————————————————————————————
# 输出结果
0 7599
1 362
2 50
dtype: int64长尾数据所在的簇为0,计算非长尾数据的轮廓系数均值:
cluster_labels = clusterer.labels_
print(np.average(silhouette_samples(X, cluster_labels)[cluster_labels != 0]))
——————————————————————————————————————————————————————————————————————————————
# 输出结果
0.4909204497858037当簇数量为4时:
# 实例化,训练,并查看结果分布
n_clusters = 4
clusterer = KMeans(n_clusters=n_clusters, random_state=100)
clusterer = clusterer.fit(X)
pd.value_counts(clusterer.labels_)
————————————————————————————————————————————————————————————
# 输出结果
0 7125
3 663
2 179
1 44
dtype: int64
————————————————————————————————————————————————————————————
# 计算非长尾数据的轮廓系数均值
cluster_labels = clusterer.labels_
print(np.average(silhouette_samples(X, cluster_labels)[cluster_labels != 0]))
————————————————————————————————————————————————————————————
# 输出结果
0.4766824917258095当簇数量为5时:
# 实例化,训练,并查看结果分布
n_clusters = 5
clusterer = KMeans(n_clusters=n_clusters, random_state=100)
clusterer = clusterer.fit(X)
pd.value_counts(clusterer.labels_)
————————————————————————————————————————————————————————————
# 输出结果
2 7065
0 691
3 198
1 38
4 19
dtype: int64
————————————————————————————————————————————————————————————
# 计算非长尾数据的轮廓系数均值
cluster_labels = clusterer.labels_
print(np.average(silhouette_samples(X, cluster_labels)[cluster_labels != 2]))
————————————————————————————————————————————————————————————
# 输出结果
0.49228555254491085当簇数量为6时:
# 实例化,训练,并查看结果分布
n_clusters = 6
clusterer = KMeans(n_clusters=n_clusters, random_state=100)
clusterer = clusterer.fit(X)
pd.value_counts(clusterer.labels_)
————————————————————————————————————————————————————————————
# 输出结果
0 6806
5 799
3 252
2 99
1 36
4 19
dtype: int64
————————————————————————————————————————————————————————————
# 计算非长尾数据的轮廓系数均值
cluster_labels = clusterer.labels_
print(np.average(silhouette_samples(X, cluster_labels)[cluster_labels != 0]))
————————————————————————————————————————————————————————————
# 输出结果
0.5043196493336838当簇数量为7时:
# 实例化,训练,并查看结果分布
n_clusters = 7
clusterer = KMeans(n_clusters=n_clusters, random_state=100)
clusterer = clusterer.fit(X)
pd.value_counts(clusterer.labels_)
————————————————————————————————————————————————————————————
# 输出结果
0 6374
5 931
6 387
2 188
1 76
4 36
3 19
dtype: int64
————————————————————————————————————————————————————————————
# 计算非长尾数据的轮廓系数均值
cluster_labels = clusterer.labels_
print(np.average(silhouette_samples(X, cluster_labels)[cluster_labels != 0]))
————————————————————————————————————————————————————————————
# 输出结果
0.501667625921486当簇数量为8时:
# 实例化,训练,并查看结果分布
n_clusters = 8
clusterer = KMeans(n_clusters=n_clusters, random_state=100)
clusterer = clusterer.fit(X)
pd.value_counts(clusterer.labels_)
————————————————————————————————————————————————————————————
# 输出结果
0 6411
5 927
4 372
2 172
6 74
1 32
7 13
3 10
dtype: int64
————————————————————————————————————————————————————————————
# 计算非长尾数据的轮廓系数均值
cluster_labels = clusterer.labels_
print(np.average(silhouette_samples(X, cluster_labels)[cluster_labels != 0]))
————————————————————————————————————————————————————————————
# 输出结果
0.4974116370311323对比上述结果,当n_clusters=6时,轮廓系数均值存在最大值0.5043;
这时查看质心的坐标:
# 设置参数n_clusters=6再次训练模型
n_clusters = 6
clusterer = KMeans(n_clusters=n_clusters, random_state=100)
clusterer = clusterer.fit(X)
# 使用属性cluster_centers_查看质心坐标
clusterer.cluster_centers_
——————————————————————————————————————————————————————————————
# 输出结果
array([[2.50559675e+02, 5.95944755e-01, 1.51620923e+02],
[4.36372269e+04, 4.83333333e+01, 2.06111111e+01],
[2.23257222e+04, 2.73232323e+01, 1.72020202e+01],
[1.15493973e+04, 1.65515873e+01, 1.95833333e+01],
[7.57037853e+04, 7.84736842e+01, 1.52631579e+01],
[4.25642288e+03, 6.82227785e+00, 4.39336671e+01]])
——————————————————————————————————————————————————————————————
# 查看聚类结果分布
pd.value_counts(clusterer.labels_)
——————————————————————————————————————————————————————————————
# 输出结果
0 6806
5 799
3 252
2 99
1 36
4 19
dtype: int64
——————————————————————————————————————————————————————————————
# 聚类结果分布以百分比形式显示
pd.value_counts(clusterer.labels_,nORMalize=True)
——————————————————————————————————————————————————————————————
# 输出结果
0 0.849582
5 0.099738
3 0.031457
2 0.012358
1 0.004494
4 0.002372
dtype: float64从结果可得(数据结果为科学计数法),6个类别客户的画像特征分别对应着:
到此这篇关于利用python实现K-Means聚类的文章就介绍到这了,更多相关Python实现K-Means聚类内容请搜索编程网以前的文章或继续浏览下面的相关文章希望大家以后多多支持编程网!
--结束END--
本文标题: 利用Python实现K-Means聚类的方法实例(案例:用户分类)
本文链接: https://lsjlt.com/news/125937.html(转载时请注明来源链接)
有问题或投稿请发送至: 邮箱/279061341@qq.com QQ/279061341
2024-03-01
2024-03-01
2024-03-01
2024-02-29
2024-02-29
2024-02-29
2024-02-29
2024-02-29
2024-02-29
2024-02-29
回答
回答
回答
回答
回答
回答
回答
回答
回答
回答
0